(Researchers report progress on molecular data storage system)
2020-02-04 アメリカ合衆国・ブラウン大学
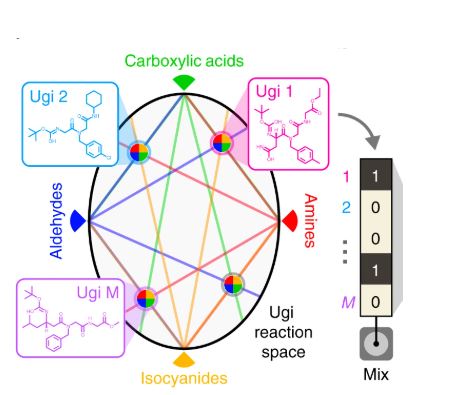
Multicomponent reactions such as the four-component Ugi reaction can generate diverse libraries of small molecules.
・ ブラウン大学が、新タイプの分子情報ストレージシステム開発の進展について報告。
・ カスタム合成した小型分子の混合物のアレイに、合計で 200 キロバイト分の画像ファイルを貯蔵して同システムを実証。小型分子を利用したデータストレージでは最大のデータ量となる。従来のデータ貯蔵技術に比較すると少量だが、小型分子ストレージ技術における飛躍的な進展と考える。
・ 分子にデータをエンコードすることで、数 mm のスペースにテラバイト規模のデータ貯蔵が可能となる。分子ストレージ研究の多くでは、DNA のような長鎖のポリマーが中心となっているが、小型分子は合成 DNA に比hして製造がより安価で容易となる可能性がある上、理論貯蔵容量がより大きい。
・ 同システムでのデータの貯蔵には、直径 1mm を下回る 1.500 個の微小な穴のアレイをもつ金属マイクロプレートを使用。各穴に収容された混合物中の特定の分子の有無により、デジタルデータが示される。各混合物のビット数は混合用の分子のライブラリの大きさに相当し、質量分析計によりデータを読み取る。
・ 同大学は昨年、一般的な代謝物を使用してキロバイト規模のイメージファイルの貯蔵を実証。今回は、独自の分子を合成することでライブラリのサイズを大幅に拡張。それにより、エンコードできるファイルのサイズも拡大できた。
・ 独自の分子の合成には、医薬品産業で多様な化合物の迅速な製造に利用されるウギ反応を利用。同反応では、アミン、アルデヒドまたはケトン、カルボキシル酸、イソニトリルの 4 種類の基質を組合せて 1 個の分子を作る。各種類の様々な基質を使用することで、多種多様な分子を迅速に合成できる。
・ 本研究では、5 種類のアミン、5 種類のアルデヒド、12 種類のカルボキシル酸と 5 種類のイソニトリルを様々に組み合わせ、1,500 個の分子のライブラリを一日で作製。ライブラリのこのようなスケーラビリティーは有利な点と考える。
・ 貯蔵対象の各イメージのエンコードにはサブライブラリを使用。32 個の分子のライブラリにエジプト神話のアヌビスのバイナリイメージを、575 個のライブラリに 0.88 メガピクセルのピカソによるバイオリンの絵のイメージを貯蔵した。
・ 同分子ライブラリの設計とデータの読み取り方法には、ある程度のエラーを訂正する余剰な情報が含まれており、これが今回の実験のワークフローの合理化を助け、99%の精度を達成できた。
・ 同システムの実用化にはさらに研究を進める必要があるが、大規模なライブラリが作製できることと、より大きなファイルのエンコードにそれらを使用できることから、同ストレージ手法は確実にスケールアップが可能と考える。
・ 本研究には、米国防高等研究計画局(DARPA)および米国立科学財団(NSF)が資金を提供した。
URL: https://www.brown.edu/news/2020-02-04/molecules
(関連情報)
Nature Communications 掲載論文(フルテキスト)
Multicomponent molecular memory
URL: https://www.nature.com/articles/s41467-020-14455-1
<NEDO海外技術情報より>
Abstract
Multicomponent reactions enable the synthesis of large molecular libraries from relatively few inputs. This scalability has led to the broad adoption of these reactions by the pharmaceutical industry. Here, we employ the four-component Ugi reaction to demonstrate that multicomponent reactions can provide a basis for large-scale molecular data storage. Using this combinatorial chemistry we encode more than 1.8 million bits of art historical images, including a Cubist drawing by Picasso. Digital data is written using robotically synthesized libraries of Ugi products, and the files are read back using mass spectrometry. We combine sparse mixture mapping with supervised learning to achieve bit error rates as low as 0.11% for single reads, without library purification. In addition to improved scaling of non-biological molecular data storage, these demonstrations offer an information-centric perspective on the high-throughput synthesis and screening of small-molecule libraries.